TensorFlowでmodelを保存して復元する
modelの保存と復元は、それぞれ以下のようにシンプルな設計で行える。
- Save a model
saver = tf.train.Saver()
saver.save(sess, '../model/test_model')
- Restore a model
saver = tf.train.Saver()
saver.restore(sess, '../model/test_model')
本記事では、実際にmodelを訓練して保存し、そのmodelを復元して、各々のテスト精度が一致していることを確認する。
処理の流れ
# coding: utf-8 import tensorflow as tf import random import os from data_fizzbuzz import DataFizzBuzz class Test: def __init__(self): pass def main(self): data = DataFizzBuzz().main() model = self.design_model(data) self.save_model(data, model) self.restore_model(data, model)
データを取得して、モデルをデザインして、モデルを訓練して保存して、モデルを復元する。
データ
例によって、FizzBuzz問題のためのデータを利用する。 ここ にあるので、以下で解説するソースと同じ場所に置く。
モデル
def design_model(self, data): X = tf.placeholder(tf.float32, [None, data[0].shape[1]]) W1 = tf.Variable(tf.truncated_normal([data[0].shape[1], 100], stddev=0.01), name='W1') B1 = tf.Variable(tf.zeros([100]), name='B1') H1 = tf.nn.tanh(tf.matmul(X, W1) + B1) W2 = tf.Variable(tf.random_normal([100, data[1].shape[1]], stddev=0.01), name='W2') B2 = tf.Variable(tf.zeros([data[1].shape[1]]), name='B2') Y = tf.matmul(H1, W2) + B2 Y_ = tf.placeholder(tf.float32, [None, data[1].shape[1]]) tf.add_to_collection('vars', W1) tf.add_to_collection('vars', B1) tf.add_to_collection('vars', W2) tf.add_to_collection('vars', B2) model = {'X': X, 'Y': Y, 'Y_': Y_} return model
1層のFFNNを訓練する。 重み(W)とバイアス(B)についてはnameを付ける。 add_to_collection()で変数として登録する。
モデルの保存
def save_model(self, data, model): """ # Data dataは、訓練データ、訓練ラベル、テストデータ、 テストラベルの順に格納されているので、順に取り出す。 """ train_data = data[0] train_label = data[1] test_data = data[2] test_label = data[3] """ # Model 設計したモデルのうち、訓練で使うのは、X, Y, Y_のみなので、それらを取り出す。 """ X, Y, Y_ = model['X'], model['Y'], model['Y_'] """ # Functions 訓練で利用する関数をそれぞれ定義する。 """ loss = tf.reduce_mean(tf.nn.softmax_cross_entropy_with_logits(Y, Y_)) step = tf.train.AdamOptimizer(0.05).minimize(loss) accuracy = tf.reduce_mean(tf.cast(tf.equal(tf.argmax(Y, 1), tf.argmax(Y_, 1)), tf.float32)) """ # Setting 初期化。saverは、モデルを保存するためのインスタンス。 """ saver = tf.train.Saver() sess = tf.Session() sess.run(tf.global_variables_initializer()) """ # Randamize data 101〜1023のデータをランダマイズする。 """ p = np.random.permutation(range(len(train_data))) train_data, train_label = train_data[p], train_label[p] """ # Training 100バッチずつ訓練するエポックを1回繰り返す。 訓練エラー、訓練精度、テスト精度を算出する。 """ for start in range(0, train_label.shape[0], 1): end = start + 100 sess.run(step, feed_dict={X: train_data[start:end], Y_: train_label[start:end]}) # Testing train_loss = sess.run(loss, feed_dict={X: train_data, Y_: train_label}) train_accuracy = sess.run(accuracy, feed_dict={X: train_data, Y_: train_label}) test_accuracy = sess.run(accuracy, feed_dict={X: test_data, Y_: test_label}) """ # Accuracy 学習後、訓練エラー、訓練精度、テスト精度を標準出力する。 """ std_output = 'Train Loss: %s, \t Train Accuracy: %s, \t Test Accuracy: %s' print(std_output % (train_loss, train_accuracy, test_accuracy)) """ # Save a model 既存の訓練モデルを削除して、今回訓練したモデルを保存する。 """ for f in os.listdir('../model/'): os.remove('../model/'+f) saver.save(sess, '../model/test_model') print('Saved a model.') sess.close()
modelディレクトリーには、以下が保存される。
- checkpoint
- test_model.data-00000-of-00001
- test_model.index
- test_model.meta
モデルの復元
def restore_model(self, data, model): # Data train_data = data[0] train_label = data[1] test_data = data[2] test_label = data[3] # Model X, Y, Y_ = model['X'], model['Y'], model['Y_'] # Function accuracy = tf.reduce_mean(tf.cast(tf.equal(tf.argmax(Y, 1), tf.argmax(Y_, 1)), tf.float32)) """ # Setting SaverとSessionのインスタンスを生成し、モデルを復元する。 """ saver = tf.train.Saver() sess = tf.Session() saver.restore(sess, '../model/test_model') print('Restored a model') test_accuracy = sess.run(accuracy, feed_dict={X: test_data, Y_: test_label}) print('Test Accuracy: %s' % test_accuracy)
復元は非常に簡単。 モデルの保存で使用したデータとモデルを渡している。 データは何でもいいが、モデルは同じものが必要。 初期化は不要。
実行結果
$ python test.py Train Loss: 1.88192, Train Accuracy: 0.781148, Test Accuracy: 0.762376 Saved a model. Restored a model Test Accuracy: 0.762376
Test Accuracyが、モデルの保存とモデルの復元で一致している。 同じモデルとテストデータだと、同じ精度が出ることが確認できた。
その他
もしモデルの復元で失敗するときは、モデルの保存を一回した後で、モデルの復元だけ実行したり、 以下のように1行足してみると上手く行くかも。
# Setting saver = tf.train.Saver() sess = tf.Session() saver = tf.train.import_meta_graph('../model/test_model.meta') ## <- add saver.restore(sess, '../model/test_model')
遺伝的アルゴリズムによるナップサック問題の最適化
以前、 遺伝的アルゴリズムの入門的なOneMax問題を解いた。
今回は、これよりも少し複雑なナップサック問題を解く。
ナップサック問題とは
Wikipedia によると、ナップサック問題とは次のような問題である。
ナップサック問題は、計算複雑性理論における計算の難しさの議論の対象となる問題の一つで、 「容量 C のナップサックが一つと、n 種類の品物(各々、価値 pi, 容積 ci)が与えられたとき、 ナップサックの容量 Cを超えない範囲でいくつかの品物をナップサックに詰め、 ナップサックに入れた品物の価値の和を最大化するにはどの品物を選べばよいか」という整数計画問題である。 同じ種類の品物を1つまでしか入れられない場合(xi ∈ {0, 1})や、 同じ品物をいくつでも入れてよい場合(xi ∈ 0以上の整数)など、いくつかのバリエーションが存在する。
今回は容量Cは無視する。 いくらでも品物を詰め込めるが、価値を最大化しつつ、容積ではなく重さを最小化する。 また同じ品物をいくつでも入れて良いことにする。
個体生成、評価、エリート選出
品物が価値と重さという2つの変数を持つ。 まずはこれらを20個生成する。
# input for i in xrange(N_ITEMS): self.items[i] = (random.randint(0, 100), random.randint(1, 10)) # value, weight
# output {0: (90, 5), 1: (18, 5), 2: (25, 7), 3: (12, 7), 4: (52, 2), 5: (77, 10), 6: (72, 3), 7: (2, 10), 8: (89, 6), 9: (36, 10), 10: (22, 9), 11: (47, 6), 12: (45, 3), 13: (65, 6), 14: (25, 6), 15: (71, 5), 16: (81, 9), 17: (11, 6), 18: (90, 10), 19: (32, 5)}
20個の品物の中から5つずつランダムに選んだセットを20個用意する。
# input pop = [] for i in range(N_POP): ind = [self.items[k] for k in random.sample(range(N_ITEMS), 5)] pop.append(ind)
# output [(25, 7), (11, 6), (2, 10), (18, 5), (77, 10)] [(22, 9), (65, 6), (77, 10), (89, 6), (81, 9)] [(72, 3), (81, 9), (52, 2), (25, 6), (18, 5)] [(36, 10), (45, 3), (81, 9), (90, 5), (90, 10)] [(25, 6), (81, 9), (36, 10), (89, 6), (77, 10)] [(65, 6), (72, 3), (90, 5), (25, 6), (12, 7)] [(18, 5), (2, 10), (71, 5), (11, 6), (36, 10)] [(77, 10), (12, 7), (25, 6), (47, 6), (71, 5)] [(89, 6), (47, 6), (25, 7), (65, 6), (25, 6)] [(52, 2), (25, 6), (18, 5), (36, 10), (89, 6)] [(71, 5), (65, 6), (36, 10), (25, 6), (32, 5)] [(2, 10), (32, 5), (25, 6), (81, 9), (71, 5)] [(12, 7), (36, 10), (71, 5), (22, 9), (81, 9)] [(36, 10), (18, 5), (12, 7), (90, 10), (72, 3)] [(77, 10), (22, 9), (90, 5), (25, 6), (11, 6)] [(22, 9), (89, 6), (71, 5), (72, 3), (65, 6)] [(77, 10), (32, 5), (52, 2), (89, 6), (45, 3)] [(47, 6), (2, 10), (18, 5), (25, 6), (89, 6)] [(65, 6), (2, 10), (89, 6), (52, 2), (45, 3)] [(36, 10), (11, 6), (2, 10), (89, 6), (65, 6)]
これらの個体として、各々評価を行う。 と言っても、価格と重さを各々足し合わせるだけ。
# input def clac_score(self, indivisual): dic = {} dic['score0'] = 0 # value dic['score1'] = 0 # weight for ind in indivisual: dic['score0'] += ind[0] dic['score1'] += ind[1]
# output {'score0': 133, 'score1': 38, 'param': [(25, 7), (11, 6), (2, 10), (18, 5), (77, 10)]} {'score0': 334, 'score1': 40, 'param': [(22, 9), (65, 6), (77, 10), (89, 6), (81, 9)]} {'score0': 248, 'score1': 25, 'param': [(72, 3), (81, 9), (52, 2), (25, 6), (18, 5)]} {'score0': 342, 'score1': 37, 'param': [(36, 10), (45, 3), (81, 9), (90, 5), (90, 10)]} {'score0': 308, 'score1': 41, 'param': [(25, 6), (81, 9), (36, 10), (89, 6), (77, 10)]} {'score0': 264, 'score1': 27, 'param': [(65, 6), (72, 3), (90, 5), (25, 6), (12, 7)]} {'score0': 138, 'score1': 36, 'param': [(18, 5), (2, 10), (71, 5), (11, 6), (36, 10)]} {'score0': 232, 'score1': 34, 'param': [(77, 10), (12, 7), (25, 6), (47, 6), (71, 5)]} {'score0': 251, 'score1': 31, 'param': [(89, 6), (47, 6), (25, 7), (65, 6), (25, 6)]} {'score0': 220, 'score1': 29, 'param': [(52, 2), (25, 6), (18, 5), (36, 10), (89, 6)]} {'score0': 229, 'score1': 32, 'param': [(71, 5), (65, 6), (36, 10), (25, 6), (32, 5)]} {'score0': 211, 'score1': 35, 'param': [(2, 10), (32, 5), (25, 6), (81, 9), (71, 5)]} {'score0': 222, 'score1': 40, 'param': [(12, 7), (36, 10), (71, 5), (22, 9), (81, 9)]} {'score0': 228, 'score1': 35, 'param': [(36, 10), (18, 5), (12, 7), (90, 10), (72, 3)]} {'score0': 225, 'score1': 36, 'param': [(77, 10), (22, 9), (90, 5), (25, 6), (11, 6)]} {'score0': 319, 'score1': 29, 'param': [(22, 9), (89, 6), (71, 5), (72, 3), (65, 6)]} {'score0': 295, 'score1': 26, 'param': [(77, 10), (32, 5), (52, 2), (89, 6), (45, 3)]} {'score0': 181, 'score1': 33, 'param': [(47, 6), (2, 10), (18, 5), (25, 6), (89, 6)]} {'score0': 253, 'score1': 27, 'param': [(65, 6), (2, 10), (89, 6), (52, 2), (45, 3)]} {'score0': 203, 'score1': 38, 'param': [(36, 10), (11, 6), (2, 10), (89, 6), (65, 6)]}
価格を最大化して、重さを最小化するには、 価格を降順、重さを昇順にソートする。 pure pythonだとソートコードが複雑になりそうだったので、Pandasを利用した。
# input df = pd.DataFrame(fitness) df = df.sort(['score0', 'score1'], ascending=[False, True])
# output param score0 score1 3 [(36, 10), (45, 3), (81, 9), (90, 5), (90, 10)] 342 37 1 [(22, 9), (65, 6), (77, 10), (89, 6), (81, 9)] 334 40 15 [(22, 9), (89, 6), (71, 5), (72, 3), (65, 6)] 319 29 4 [(25, 6), (81, 9), (36, 10), (89, 6), (77, 10)] 308 41 16 [(77, 10), (32, 5), (52, 2), (89, 6), (45, 3)] 295 26 5 [(65, 6), (72, 3), (90, 5), (25, 6), (12, 7)] 264 27 18 [(65, 6), (2, 10), (89, 6), (52, 2), (45, 3)] 253 27 8 [(89, 6), (47, 6), (25, 7), (65, 6), (25, 6)] 251 31 2 [(72, 3), (81, 9), (52, 2), (25, 6), (18, 5)] 248 25 7 [(77, 10), (12, 7), (25, 6), (47, 6), (71, 5)] 232 34 10 [(71, 5), (65, 6), (36, 10), (25, 6), (32, 5)] 229 32 13 [(36, 10), (18, 5), (12, 7), (90, 10), (72, 3)] 228 35 14 [(77, 10), (22, 9), (90, 5), (25, 6), (11, 6)] 225 36 12 [(12, 7), (36, 10), (71, 5), (22, 9), (81, 9)] 222 40 9 [(52, 2), (25, 6), (18, 5), (36, 10), (89, 6)] 220 29 11 [(2, 10), (32, 5), (25, 6), (81, 9), (71, 5)] 211 35 19 [(36, 10), (11, 6), (2, 10), (89, 6), (65, 6)] 203 38 17 [(47, 6), (2, 10), (18, 5), (25, 6), (89, 6)] 181 33 6 [(18, 5), (2, 10), (71, 5), (11, 6), (36, 10)] 138 36 0 [(25, 7), (11, 6), (2, 10), (18, 5), (77, 10)] 133 38
ただし、populationはdict in listで扱いたいので、 DataFrameから再びdict in listに変換している。
# input fitness = df.to_dict('records')
# output {'score0': 342, 'score1': 37, 'param': [(36, 10), (45, 3), (81, 9), (90, 5), (90, 10)]} {'score0': 334, 'score1': 40, 'param': [(22, 9), (65, 6), (77, 10), (89, 6), (81, 9)]} {'score0': 319, 'score1': 29, 'param': [(22, 9), (89, 6), (71, 5), (72, 3), (65, 6)]} {'score0': 308, 'score1': 41, 'param': [(25, 6), (81, 9), (36, 10), (89, 6), (77, 10)]} {'score0': 295, 'score1': 26, 'param': [(77, 10), (32, 5), (52, 2), (89, 6), (45, 3)]} {'score0': 264, 'score1': 27, 'param': [(65, 6), (72, 3), (90, 5), (25, 6), (12, 7)]} {'score0': 253, 'score1': 27, 'param': [(65, 6), (2, 10), (89, 6), (52, 2), (45, 3)]} {'score0': 251, 'score1': 31, 'param': [(89, 6), (47, 6), (25, 7), (65, 6), (25, 6)]} {'score0': 248, 'score1': 25, 'param': [(72, 3), (81, 9), (52, 2), (25, 6), (18, 5)]} {'score0': 232, 'score1': 34, 'param': [(77, 10), (12, 7), (25, 6), (47, 6), (71, 5)]} {'score0': 229, 'score1': 32, 'param': [(71, 5), (65, 6), (36, 10), (25, 6), (32, 5)]} {'score0': 228, 'score1': 35, 'param': [(36, 10), (18, 5), (12, 7), (90, 10), (72, 3)]} {'score0': 225, 'score1': 36, 'param': [(77, 10), (22, 9), (90, 5), (25, 6), (11, 6)]} {'score0': 222, 'score1': 40, 'param': [(12, 7), (36, 10), (71, 5), (22, 9), (81, 9)]} {'score0': 220, 'score1': 29, 'param': [(52, 2), (25, 6), (18, 5), (36, 10), (89, 6)]} {'score0': 211, 'score1': 35, 'param': [(2, 10), (32, 5), (25, 6), (81, 9), (71, 5)]} {'score0': 203, 'score1': 38, 'param': [(36, 10), (11, 6), (2, 10), (89, 6), (65, 6)]} {'score0': 181, 'score1': 33, 'param': [(47, 6), (2, 10), (18, 5), (25, 6), (89, 6)]} {'score0': 138, 'score1': 36, 'param': [(18, 5), (2, 10), (71, 5), (11, 6), (36, 10)]} {'score0': 133, 'score1': 38, 'param': [(25, 7), (11, 6), (2, 10), (18, 5), (77, 10)]}
個体と評価を保存する
ナップサック問題の個体の評価は、各品物の価格と重さを各々足し合わせるだけなので高速だが、 遺伝的アルゴリズムが扱う問題によっては評価に時間がかかることがある。 世代を重ねるごとに各個体は評価が上がり類似した遺伝子になっていく。 そのため、交叉や突然変異により生成された個体と同じ遺伝子を持つ個体が過去に存在することも珍しくない。 今後の遺伝的アルゴリズムの拡張を考えて、過去の個体とその評価を保存し、各個体を評価する前に参照するようにしておく。
保存する形式もdict in listにするが、パラメーターがlistだと一致評価できないので、Stringに変換してから保存。
self.fitness_master = {}
for fit in fitness:
param = fit['param']
self.fitness_master[str(param)] = {k:v for k,v in fit.items() if k!='param'}
個体の評価では、次の3パターンに別れる。
- スコアはないけどパラメーターはある
- スコアもなくてパラメーターもない
- スコアもパラメーターもある
1がまさに今回のパターン。2は新たな個体が生まれたとき。 3は交叉または突然変異の前の評価のとき。 このアルゴリズム特有で無駄な処理だが、個体の評価を参照することで高速処理できる。
fitness = [] for p in pop: if not p.has_key('score0'): # The indivisual made by crossover or mutation existed before if self.fitness_master.has_key(str(p['param'])): p.update(self.fitness_master[str(p['param'])]) # The indivisual is the first else: p.update(self.clac_score(p['param'])) fitness.append(p) else: fitness.append(p)
まとめ
実行結果は、以下の通り。 世代数が少ない、突然変異率が低いなどが原因で、 必ずしも一番価値のある商品だけで構成するとはなっていない。
V W P Generation 0: 323 25 [(25, 1), (82, 3), (89, 6), (45, 10), (82, 5)] Generation 1: 323 25 [(25, 1), (82, 3), (89, 6), (45, 10), (82, 5)] Generation 2: 323 25 [(25, 1), (82, 3), (89, 6), (45, 10), (82, 5)] Generation 3: 365 22 [(89, 6), (65, 2), (65, 2), (82, 5), (64, 7)] Generation 4: 365 22 [(89, 6), (65, 2), (65, 2), (82, 5), (64, 7)] Generation 5: 365 22 [(89, 6), (65, 2), (65, 2), (82, 5), (64, 7)] Generation 6: 365 22 [(89, 6), (65, 2), (65, 2), (82, 5), (64, 7)] Generation 7: 389 26 [(89, 6), (65, 2), (89, 6), (82, 5), (64, 7)] Generation 8: 389 26 [(89, 6), (65, 2), (89, 6), (82, 5), (64, 7)] Generation 9: 389 26 [(89, 6), (65, 2), (89, 6), (82, 5), (64, 7)] Generation 10: 396 27 [(89, 6), (89, 6), (89, 6), (65, 2), (64, 7)] Generation 11: 396 27 [(89, 6), (89, 6), (89, 6), (65, 2), (64, 7)] Generation 12: 420 31 [(89, 6), (89, 6), (89, 6), (89, 6), (64, 7)] Generation 13: 420 31 [(89, 6), (89, 6), (89, 6), (89, 6), (64, 7)] Generation 14: 420 31 [(89, 6), (89, 6), (89, 6), (89, 6), (64, 7)] Generation 15: 420 31 [(89, 6), (89, 6), (89, 6), (89, 6), (64, 7)] Generation 16: 420 31 [(89, 6), (89, 6), (89, 6), (89, 6), (64, 7)] Generation 17: 420 31 [(89, 6), (89, 6), (89, 6), (89, 6), (64, 7)] Generation 18: 420 31 [(89, 6), (89, 6), (89, 6), (89, 6), (64, 7)] Generation 19: 420 31 [(89, 6), (89, 6), (89, 6), (89, 6), (64, 7)] Generation 20: 420 31 [(89, 6), (89, 6), (89, 6), (89, 6), (64, 7)] Generation 21: 420 31 [(89, 6), (89, 6), (89, 6), (89, 6), (64, 7)] Generation 22: 420 31 [(89, 6), (89, 6), (89, 6), (89, 6), (64, 7)] Generation 23: 420 31 [(89, 6), (89, 6), (89, 6), (89, 6), (64, 7)] Generation 24: 420 31 [(89, 6), (89, 6), (89, 6), (89, 6), (64, 7)]
全コードも載せておく。
# coding: utf-8 import random import math import copy import operator import pandas as pd N_ITEMS = 20 N_POP = 20 N_GEN = 25 MUTATE_PROB = 0.1 ELITE_RATE = 0.5 class GA: def __init__(self): self.items = {} self.fitness_master = {} def main(self): pop = [{'param': p} for p in self.get_population()] for g in range(N_GEN): print 'Generation%3s:' % str(g), # Get elites fitness = self.evaluate(pop) elites = fitness[:int(len(pop)*ELITE_RATE)] # Cross and mutate pop = elites[:] while len(pop) < N_POP: if random.random() < MUTATE_PROB: m = random.randint(0, len(elites)-1) child = self.mutate(elites[m]['param']) else: c1 = random.randint(0, len(elites)-1) c2 = random.randint(0, len(elites)-1) child = self.crossover(elites[c1]['param'], elites[c2]['param']) pop.append({'param': child}) # Evaluate indivisual fitness = self.evaluate(pop) pop = fitness[:] print pop[0]['score0'], pop[0]['score1'], pop[0]['param'] def get_population(self): # Make items for i in xrange(N_ITEMS): self.items[i] = (random.randint(0, 100), random.randint(1, 10)) # value, weight # Make population pop = [] for i in range(N_POP): ind = [self.items[k] for k in random.sample(range(N_ITEMS), 5)] pop.append(ind) return pop def clac_score(self, indivisual): dic = {} dic['score0'] = 0 # value dic['score1'] = 0 # weight for ind in indivisual: dic['score0'] += ind[0] dic['score1'] += ind[1] return dic def evaluate(self, pop): fitness = [] for p in pop: if not p.has_key('score0'): # The indivisual made by crossover or mutation existed before if self.fitness_master.has_key(str(p['param'])): p.update(self.fitness_master[str(p['param'])]) # The indivisual is the first else: p.update(self.clac_score(p['param'])) fitness.append(p) else: fitness.append(p) # Save fitness to all genaration dictinary for fit in fitness: param = fit['param'] self.fitness_master[str(param)] = {k:v for k,v in fit.items() if k!='param'} # This generation fitness df = pd.DataFrame(fitness) df = df.sort(['score0', 'score1'], ascending=[False, True]) fitness = df.to_dict('records') return fitness def mutate(self, parent): ind_idx = int(math.floor(random.random()*len(parent))) item_idx = random.choice(range(N_ITEMS)) child = copy.deepcopy(parent) child[ind_idx] = self.items[item_idx] return child def crossover(self, parent1, parent2): length = len(parent1) r1 = int(math.floor(random.random()*length)) r2 = r1 + int(math.floor(random.random()*(length-r1))) child = copy.deepcopy(parent1) child[r1:r2] = parent2[r1:r2] return child if __name__ == "__main__": GA().main()
追記: 第一世代の扱いについて
上記だと、for文の中にevaluate()が無駄に2つ入ってるが、 1つ目は第一世代の評価にしか使わないので、for文の外に出す方が適切。 for文の中では、交叉と突然変異で生まれた世代の評価を行う。
def main(self): print('Generation 1:'), pop = [{'param': p} for p in self.get_population()] fitness = self.evaluate(pop) print(fitness[0]['score0'], fitness[0]['score1'], fitness[0]['param']) for g in range(N_GEN-1): print('Generation %2s:' % str(g+2)), # Get elites elites = fitness[:int(len(pop)*ELITE_RATE)] # Cross and mutate pop = elites[:] while len(pop) < N_POP: if random.random() < MUTATE_PROB: m = random.randint(0, len(elites)-1) child = self.mutate(elites[m]['param']) else: c1 = random.randint(0, len(elites)-1) c2 = random.randint(0, len(elites)-1) child = self.crossover(elites[c1]['param'], elites[c2]['param']) pop.append({'param': child}) # Evaluate indivisual fitness = self.evaluate(pop) print(fitness[0]['score0'], fitness[0]['score1'], fitness[0]['param'])
Pandas.DataFrameをdicts in listに変換する
dicts in listからDataFrameを作成することはよくあるが、
DataFrameをdicts in listにしたい時がたまにある。
df.to_dict('records')を実行するだけで良いのだが、
このシンプルなコードを良く忘れるのに記事にした。
入出力がまったく同じdicts in listで実施。
dicts_in_list = [{'x': random.randint(0, 10), 'y': random.randint(1, 5)} for i in range(10)]
for dil in dicts_in_list:
print dil
df = pd.DataFrame(dicts_in_list)
print df
dicts_in_list = df.to_dict('records')
for dil in dicts_in_list:
print dil
結果は以下の通り。
{'y': 1, 'x': 9}
{'y': 2, 'x': 7}
{'y': 3, 'x': 7}
{'y': 1, 'x': 10}
{'y': 5, 'x': 8}
{'y': 2, 'x': 1}
{'y': 5, 'x': 0}
{'y': 5, 'x': 6}
{'y': 5, 'x': 3}
{'y': 5, 'x': 7}
x y
0 9 1
1 7 2
2 7 3
3 10 1
4 8 5
5 1 2
6 0 5
7 6 5
8 3 5
9 7 5
{'y': 1, 'x': 9}
{'y': 2, 'x': 7}
{'y': 3, 'x': 7}
{'y': 1, 'x': 10}
{'y': 5, 'x': 8}
{'y': 2, 'x': 1}
{'y': 5, 'x': 0}
{'y': 5, 'x': 6}
{'y': 5, 'x': 3}
{'y': 5, 'x': 7}
参考文献
Pandas.DataFrameの複数カラムの同時ソート
多分100回ぐらい調べてるので、いい加減覚えるために、記事を書いてみた。 ランダム生成したxとyについて、各々降順、昇順で同時にソートする。
import pandas as pd data = [{'x': random.randint(0, 10), 'y': random.randint(1, 5)} for i in range(10)] df = pd.DataFrame(data) df = df.sort(['x', 'y'], ascending=[False, True]) df.reset_index(drop=True, inplace=True) print df
xが8,4,1の場合にソートが有効になっていることが確認できる。
x y 0 10 1 1 8 3 2 8 5 3 6 5 4 4 1 5 4 2 6 4 5 7 1 1 8 1 5 9 0 4
参考文献
ラベルをOneHotでエンコードする
Deep Learning、と言ってもTensorFlowしか使ったことないけど、 ラベルがnx1(nはレコード数)の行列の場合は、OneHotにエンコードする必要がある(下図)。 scikit-learnのOneHotEncoderで、一発でエンコードできるのだが、 nx1の行列をnxm(mはラベルの値の種類)に変換する処理をnumpyで行う必要があるので実装した。
# nx1 matrix label = [4 3 0 0 1 1 1 4 3 0] # nxm matrix onehot_label = [[ 0. 0. 0. 0. 1.] [ 0. 0. 0. 1. 0.] [ 1. 0. 0. 0. 0.] [ 1. 0. 0. 0. 0.] [ 0. 1. 0. 0. 0.] [ 0. 1. 0. 0. 0.] [ 0. 1. 0. 0. 0.] [ 0. 0. 0. 0. 1.] [ 0. 0. 0. 1. 0.] [ 1. 0. 0. 0. 0.]]
実装
numpyでreshapeとtransposeを行い、 scikit-learnでonehotにencodeする。
import numpy as np from sklearn.preprocessing import OneHotEncoder # generate label. X = np.array([random.choice(range(5)) for i in range(10)]) print(X) # reshape X = np.array(X).reshape(1, -1) print(X) # transpose X = X.transpose() print(X) # encode label encoder = OneHotEncoder(n_values=max(X)+1) X = encoder.fit_transform(X).toarray() print(X)
各々の出力結果は以下の通り。
[2 0 0 4 3 3 4 4 2 3] [[2 0 0 4 3 3 4 4 2 3]] [[2] [0] [0] [4] [3] [3] [4] [4] [2] [3]] [[ 0. 0. 1. 0. 0.] [ 1. 0. 0. 0. 0.] [ 1. 0. 0. 0. 0.] [ 0. 0. 0. 0. 1.] [ 0. 0. 0. 1. 0.] [ 0. 0. 0. 1. 0.] [ 0. 0. 0. 0. 1.] [ 0. 0. 0. 0. 1.] [ 0. 0. 1. 0. 0.] [ 0. 0. 0. 1. 0.]]
参考文献
遺伝的アルゴリズムによるOneMax問題の最適化
OneMax問題とは、[1,0,0,1,0,1,1,1,1,0]のように0/1からなる数列の和を最大化する問題のこと。 答えはすべて1の数列と自明だが、これを最適化アルゴリズムの1つである遺伝的アルゴリズムで解く。 遺伝的アルゴリズムとは、このような数列を遺伝子と見立て複数生成し、 数世代に渡り交叉と突然変異を繰り返すことにより、優秀な遺伝子を生み出すアルゴリズムのこと。 ここでの優秀の定義は「数列の和が大きい」となる。
PythonではDEAPという 遺伝的アルゴリズムのライブラリーがあるが、個人的に拡張性が低くて使いにくかったのと、 実装がそれほど難しくはないので、Pythonでスクラッチから書くことにした。
アルゴリズムの流れ
- 第1世代の個体群の生成
- エリートの選択
- エリートの交叉/突然変異
- 次世代の個体群の生成
- 2〜4の操作を繰り返し、適応度の最も高い個体を解として出力
簡単な流れは上記の通り。 各世代の個体群の数は固定で、現世代のエリートと、彼らの子供の和となる。
1. 第1世代の個体群の生成
第2世代以降の個体群の生成は、基本的に交叉か突然変異になる。 そのため、この操作は第1世代だけ必要になる。 ランダム選択した0/1がN_PARAM個並ぶ数列を、 N_POP個生成する。
def get_population(self):
population = []
for i in range(N_POP):
arr = [random.randint(0,1) for j in range(N_PARAM)]
population.append(arr)
return population
各個体は後ほど適応度を計算するが、まず-1で初期化しておく。
>>> pop = [(-1, p) for p in self.get_population()]
>>> pop
[
(-1, [0, 0, 0, 0, 1, 1, 1, 1, 0, 0]),
(-1, [1, 0, 1, 0, 1, 0, 0, 1, 0, 0]),
(-1, [1, 0, 0, 0, 1, 0, 0, 0, 0, 1]),
...
]
2. エリートの選択
evaluateメソッドで、個体の適応度(fitness)を計算している。 OneMaxにおける適応度はリストの和とシンプルだが、今後の拡張を考えてメソッド化(clac_score)しておく。
def clac_score(self, x): return sum(x) def evaluate(self, pop): fitness = [] for p in pop: if p[0] == -1: fitness.append((self.clac_score(p[1]), p[1])) else: fitness.append(p) fitness.sort() fitness.reverse() return fitness
全個体の適応度を計算してソートしたら、ELITE_RATEの割合でエリートとして選択する。
>>> fitness = self.evaluate(pop) >>> elites = fitness[:int(len(pop)*ELITE_RATE)]
3. エリートの交叉/突然変異
突然変異mutate()では、個体の数列からパラメーターを1つだけ反転させる。
交叉crossover()では、片親の遺伝子の一部を切り取り、もう片親の同じ位置にペーストする。
これを2点交叉というが、場合によっては1点交叉にもなり得る。
def mutate(self, parent): r = int(math.floor(random.random()*len(parent))) child = copy.deepcopy(parent) child[r] = (parent[r]+1) % 2 return child def crossover(self, parent1, parent2): length = len(parent1) r1 = int(math.floor(random.random()*length)) r2 = r1 + int(math.floor(random.random()*(length-r1))) child = copy.deepcopy(parent1) child[r1:r2] = parent2[r1:r2] return child
突然変異はMUTATE_BROPの確率で起こり、それ以外は交叉となる。 これを全ての個体に対して行う。個体の組合せはランダムである。
pop = elites[:] while len(pop) < N_POP: if random.random() < MUTATE_PROB: m = random.randint(0, len(elites)-1) child = self.mutate(elites[m][1]) else: c1 = random.randint(0, len(elites)-1) c2 = random.randint(0, len(elites)-1) child = self.crossover(elites[c1][1], elites[c2][1]) pop.append((-1, child))
4. 次世代の個体群の生成
現世代のエリートを選択し、彼らを交叉/突然変異させた個体群を生成した。 これらの適応度を計算することで、次世代の個体群が生成される。
fitness = self.evaluate(pop) pop = fitness[:]
結果
10個の0/1の数列のOneMax問題を解かせたところ、第4世代で最適解が得られた。
Generation: 0 (8, [1, 1, 1, 1, 1, 1, 1, 0, 0, 1]) Generation: 1 (9, [1, 1, 1, 1, 1, 1, 1, 1, 0, 1]) Generation: 2 (9, [1, 1, 1, 1, 1, 1, 1, 1, 0, 1]) Generation: 3 (10, [1, 1, 1, 1, 1, 1, 1, 1, 1, 1]) ... Generation: 24 (10, [1, 1, 1, 1, 1, 1, 1, 1, 1, 1])
ソースコード
全ソースコードを以下に載せておく。1ファイルにまとまっている。$ python ga.pyで実行可能。
# coding: utf-8 import random import math import copy N_PARAM = 10 N_POP = 20 N_GEN = 25 MUTATE_PROB = 0.1 ELITE_RATE = 0.2 class GA: def __init__(self): pass def main(self): pop = [(-1, p) for p in self.get_population()] for g in range(N_GEN): print 'Generation: ' + str(g) # Get elites fitness = self.evaluate(pop) elites = fitness[:int(len(pop)*ELITE_RATE)] # Cross and mutate pop = elites[:] while len(pop) < N_POP: if random.random() < MUTATE_PROB: m = random.randint(0, len(elites)-1) child = self.mutate(elites[m][1]) else: c1 = random.randint(0, len(elites)-1) c2 = random.randint(0, len(elites)-1) child = self.crossover(elites[c1][1], elites[c2][1]) pop.append((-1, child)) # Evaluate indivisual fitness = self.evaluate(pop) pop = fitness[:] print pop[0] print def get_population(self): population = [] for i in range(N_POP): arr = [random.randint(0,1) for j in range(N_PARAM)] population.append(arr) return population def clac_score(self, x): return sum(x) def evaluate(self, pop): fitness = [] for p in pop: if p[0] == -1: fitness.append((self.clac_score(p[1]), p[1])) else: fitness.append(p) fitness.sort() fitness.reverse() return fitness def mutate(self, parent): r = int(math.floor(random.random()*len(parent))) child = copy.deepcopy(parent) child[r] = (parent[r]+1) % 2 return child def crossover(self, parent1, parent2): length = len(parent1) r1 = int(math.floor(random.random()*length)) r2 = r1 + int(math.floor(random.random()*(length-r1))) child = copy.deepcopy(parent1) child[r1:r2] = parent2[r1:r2] return child if __name__ == "__main__": GA().main()
参考文献
DeepLearningの学習曲線をmatplotlibで可視化
TensorBoardのEventsによる学習状況の可視化 を行ったが、今後いろいろとカスタマイズしたくなると思い、matplotlibで可視化することにした。 今回もFizzBuzz問題を例に扱う。詳しくは、Deep Learning入門としてのFizzBuzz問題を参照。
精度とコストの記録
学習過程(train_network())で、エポックごとにtrain_loss、train_accuracy、test_accuracyを算出して記録する。
記録はCSV形式で保存する。# Loggingと# Save logsがそれらの操作にあたる。
def train_network(self, data, network): # data train_data = data[0] train_label = data[1] test_data = data[2] test_label = data[3] # model X = network['X'] Y = network['Y'] Y_ = network['Y_'] loss = network['loss'] step = network['step'] # Setting sess = tf.InteractiveSession() tf.initialize_all_variables().run() accuracy = tf.reduce_mean(tf.cast(tf.equal(tf.argmax(Y, 1), tf.argmax(Y_, 1)), tf.float32)) logs = [] for epoch in range(N_ITER+1): # Randamize data p = np.random.permutation(range(len(train_data))) train_data, train_label = train_data[p], train_label[p] # Training for start in range(0, train_label.shape[0], BATCH_SIZE): end = start + BATCH_SIZE sess.run(step, feed_dict={X: train_data[start:end], Y_: train_label[start:end]}) # Testing train_loss = sess.run(loss, feed_dict={X: train_data, Y_: train_label}) train_accuracy = sess.run(accuracy, feed_dict={X: train_data, Y_: train_label}) test_accuracy = sess.run(accuracy, feed_dict={X: test_data, Y_: test_label}) # Logging log = {'epoch': epoch, 'train_loss': train_loss, 'train_accuracy': train_accuracy, 'test_accuracy': test_accuracy} logs.append(log) if epoch % 100 == 0: std_output = 'Epoch: %s, \t Train Loss: %s, \t Train Accuracy: %s, \t Test Accuracy: %s' print(std_output % (log['epoch'], log['train_loss'], log['train_accuracy'], log['test_accuracy'])) # Save logs df = pd.DataFrame(logs) df.to_csv("./log/acculoss_train_%s_batch_%s_iter_%s.csv" % (TRAIN_RATE, BATCH_SIZE, N_ITER), index=False)
CSVファイルは以下のようになる。
epoch,test_accuracy,train_accuracy,train_loss 0,0.5247524976730347,0.5341278314590454,1.3275593519210815 1,0.5247524976730347,0.5341278314590454,1.284529209136963 2,0.5247524976730347,0.5341278314590454,1.2487729787826538 ... 9998,0.9801980257034302,1.0,0.008503337390720844 9999,0.9801980257034302,1.0,0.008444004692137241 10000,0.9801980257034302,1.0,0.008517774753272533
可視化
保存したCSVファイルを読み込んで、精度とコストの値をセットして、 背景色がグレーなのが気に入らないのでホワイトにして、各曲線にラベルを付けて、可視化を行う。
def main(self): # Read file df = pd.read_csv('./log/acculoss_train_0.05_batch_100_iter_10000.csv') # Set values x = df['epoch'].values y0 = df['train_loss'].values y1 = df['train_accuracy'].values y2 = df['test_accuracy'].values # Set background color to white fig = plt.figure() fig.patch.set_facecolor('white') # Plot lines plt.xlabel('epoch') plt.plot(x, y0, label='train_loss') plt.plot(x, y1, label='train_accuracy') plt.plot(x, y2, label='test_accuracy') plt.legend() # Visualize plt.show()
可視化すると以下のようになる。
train_accuracyとtrain_lossだけを見ると上手くいってるように見えるが、
test_accuracyを見ると過学習しているのが分かる。
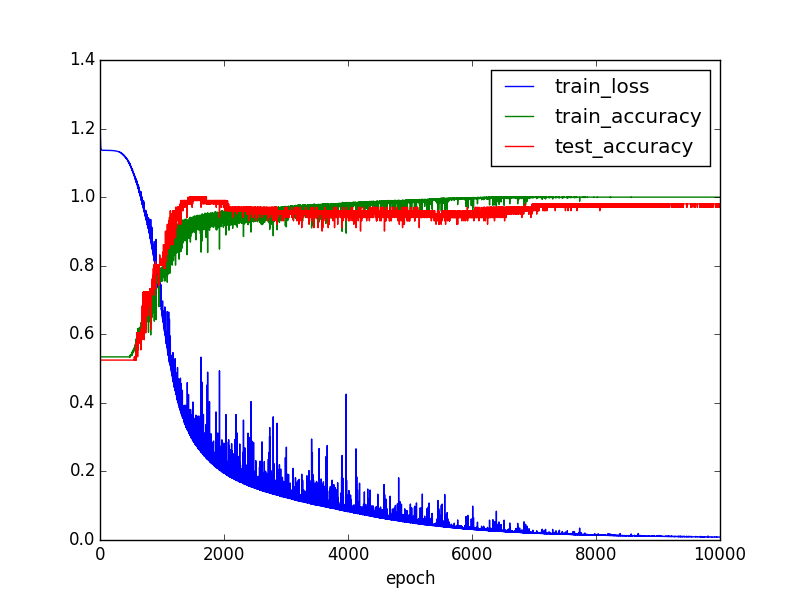
ちなみに最終結果は、以下の通り、まあまあの精度。
| Epoch | Train Loss | Train Accuracy | Test Accuracy |
|---|---|---|---|
| 10000 | 0.00851777 | 1.0 | 0.980198 |